2019年9月29日 星期日
2019年9月28日 星期六
2019年9月27日 星期五
ubuntu 18.04 nvidia-driver-435 E: Unable to correct problems, you have held broken packages.
這是因為顯卡驅動沒有清除乾淨,所以如果要用sudo ubuntu-drivers autoinstall安裝顯卡驅動之前要在終端機先執行以下指令
$ sudo apt remove --purge nvidia*
參考
https://ubuntuforums.org/showthread.php?t=2417585
2019年9月25日 星期三
2019年9月24日 星期二
2019年9月23日 星期一
2019年9月22日 星期日
2019年9月21日 星期六
ubuntu 18.04 install tensorflow 1.14.0
安裝tensorflow之前要先確認python3、pip、pip3的環境設定,由於我們在執行tensorflow或Keras都是呼叫python3,所以我們必須確認pip、pip3哪個環境設定是和python3相同,否則在安裝tensorflow以及Keras會發生找不到Module的情形發生。
ubuntu 18.04 install cuDNN
NVIDIACUDA®深度神經網路函式庫(cuDNN)是GPU加速的用於深度神經網絡的原語庫。 cuDNN在執行上提供了高度優化的能力,像是在forward和backward卷積,池化,normalization和activation layers。以下是安裝流程:
2019年9月20日 星期五
PBS
鳥哥 簡易 Cluster 架設
http://linux.vbird.org/linux_server/0600cluster.php
鳥哥的 Linux 私房菜 -- 伺服器架設篇目錄http://linux.vbird.org/linux_server/index_old.php
Centos 7詳細網站
https://www.server-world.info/en/note?os=CentOS_7&p=nis&f=1
CentOS下torque集群配置
https://blog.csdn.net/Dream_angel_Z/article/details/44225669
https://blog.csdn.net/Dream_angel_Z/article/details/44225713
https://blog.csdn.net/Dream_angel_Z/article/details/44226055?locationNum=8&fps=1
https://blog.csdn.net/dream_angel_z/article/details/44226179
PBS script
https://csc.cnsi.ucsb.edu/docs/example-scripts-running-jobs
NFS為Network File System,可以把本地的目錄共享給指定IP域的主機,想要訪問共享目錄的主機可以將共享目錄掛在到本地進行直接訪問
http://linux.vbird.org/linux_server/0330nfs.php
https://qizhanming.com/blog/2018/08/08/how-to-install-nfs-on-centos-7
NIS為Network Information Service,可以為多態用戶創建統一的用戶登錄機制,使多個主機可以使用相同的用戶登錄到網絡中,對共享目錄進行讀寫操作
http://linux.vbird.org/linux_server/0430nis.php
https://blog.csdn.net/younger_china/article/details/53130780
RSH
在我們的 Linux 主機上面工作,通常使用 BASH 這個 shell 來傳達給 kernel 工作的訊息,以使主機正確的工作;而如果在不同的主機之間,那就可以使用 R Shell 來進行指令的下達喔,如此一來,我們就可以直接在 A 機器,向 B 機器下達工作的指令,而不需要登入 B 機器呢~那就是 RSH 的主要功能啦!最常見的 RSH 指令就是 rcp 與 rsh 了!有興趣的朋友應該知道以 man 來查尋一下該指令的用法囉!
需要附帶一提的是,這個 RSH 是『相當危險』的一個服務喔!由於我們可以直接登入 RSH 主機,並且在上面進行指令的下達,為了避免還要輸入密碼的問題,因此通常 RSH 已經將信任主機設定好了,不過,由於 RSH 會啟動一些 port 來監聽 Clients 的需求,而偏偏這些 port 與 daemon 都還挺危險的,因此,『Cluster 最好是設定在內部網域當中,並使用私有 IP ,比較能夠避免危險』喔!此外,那個 Master 也必須要設定好一定程度的嚴密防火牆喔!
http://linux.vbird.org/linux_server/0600cluster.php
Installing Torque 6.0.1 on CentOS 7
https://www.webmo.net/support/torque.html
Centos下搭建MPI集群計算環境
https://www.iczc.me/post/building-an-MPI-cluster-with-Centos/
https://www.webmo.net/support/torque.html
https://www.wandouip.com/t5i267150/
http://blog.sciencenet.cn/blog-548899-720364.html
http://staff.pccu.edu.tw/~lchou/reference/cluster_doc/ClusteringQueueingSystem(Cmeta).pdf
https://wiki.archlinux.org/index.php/TORQUE#NFS
http://linux.vbird.org/linux_server/0600cluster.php
鳥哥的 Linux 私房菜 -- 伺服器架設篇目錄http://linux.vbird.org/linux_server/index_old.php
Centos 7詳細網站
https://www.server-world.info/en/note?os=CentOS_7&p=nis&f=1
CentOS下torque集群配置
https://blog.csdn.net/Dream_angel_Z/article/details/44225669
https://blog.csdn.net/Dream_angel_Z/article/details/44225713
https://blog.csdn.net/Dream_angel_Z/article/details/44226055?locationNum=8&fps=1
https://blog.csdn.net/dream_angel_z/article/details/44226179
PBS script
https://csc.cnsi.ucsb.edu/docs/example-scripts-running-jobs
NFS為Network File System,可以把本地的目錄共享給指定IP域的主機,想要訪問共享目錄的主機可以將共享目錄掛在到本地進行直接訪問
http://linux.vbird.org/linux_server/0330nfs.php
https://qizhanming.com/blog/2018/08/08/how-to-install-nfs-on-centos-7
NIS為Network Information Service,可以為多態用戶創建統一的用戶登錄機制,使多個主機可以使用相同的用戶登錄到網絡中,對共享目錄進行讀寫操作
http://linux.vbird.org/linux_server/0430nis.php
https://blog.csdn.net/younger_china/article/details/53130780
RSH
在我們的 Linux 主機上面工作,通常使用 BASH 這個 shell 來傳達給 kernel 工作的訊息,以使主機正確的工作;而如果在不同的主機之間,那就可以使用 R Shell 來進行指令的下達喔,如此一來,我們就可以直接在 A 機器,向 B 機器下達工作的指令,而不需要登入 B 機器呢~那就是 RSH 的主要功能啦!最常見的 RSH 指令就是 rcp 與 rsh 了!有興趣的朋友應該知道以 man 來查尋一下該指令的用法囉!
需要附帶一提的是,這個 RSH 是『相當危險』的一個服務喔!由於我們可以直接登入 RSH 主機,並且在上面進行指令的下達,為了避免還要輸入密碼的問題,因此通常 RSH 已經將信任主機設定好了,不過,由於 RSH 會啟動一些 port 來監聽 Clients 的需求,而偏偏這些 port 與 daemon 都還挺危險的,因此,『Cluster 最好是設定在內部網域當中,並使用私有 IP ,比較能夠避免危險』喔!此外,那個 Master 也必須要設定好一定程度的嚴密防火牆喔!
http://linux.vbird.org/linux_server/0600cluster.php
Installing Torque 6.0.1 on CentOS 7
https://www.webmo.net/support/torque.html
Centos下搭建MPI集群計算環境
https://www.iczc.me/post/building-an-MPI-cluster-with-Centos/
https://www.webmo.net/support/torque.html
https://www.wandouip.com/t5i267150/
http://blog.sciencenet.cn/blog-548899-720364.html
http://staff.pccu.edu.tw/~lchou/reference/cluster_doc/ClusteringQueueingSystem(Cmeta).pdf
https://wiki.archlinux.org/index.php/TORQUE#NFS
2019年9月19日 星期四
2019年9月17日 星期二
2019年9月16日 星期一
Generating Molecules with the Help of Recurrent Neural Networks
傳統藥物開發分兩個階段進行; 發現階段和發展階段。 一旦發現某種疾病的目標或根本原因/機制,我們需要識別化合物並驗證這些化合物是否可以阻止或抑制這些疾病的活動。 對於每5000種化合物測試,只有一種具有初始的積極效果,對於那些我們對其毒性或其他生理化學特徵沒有基本了解的化合物。 這使得工作漫長而艱鉅,幾乎沒有結果。 與此同時,數百萬人正在死於這些疾病。 這主要是因為為什麼投資大多數製藥公司不如將您的儲蓄存入高息賬戶。
但是,我們如何嘗試加速我們識別某些目標效應的化合物的方式? 在這種情況下,這就是生成網絡領域迅速普及,以幫助使用諸如RNN之類的網絡生成新分子的地方。 目標是通過去除盡可能多的過程來加速發現階段的過程,我們必須通過重新藥物設計(de novo drug design)手動測試大量化合物來識別有效的化合物。
Project De Novo: Generating Novel Molecules
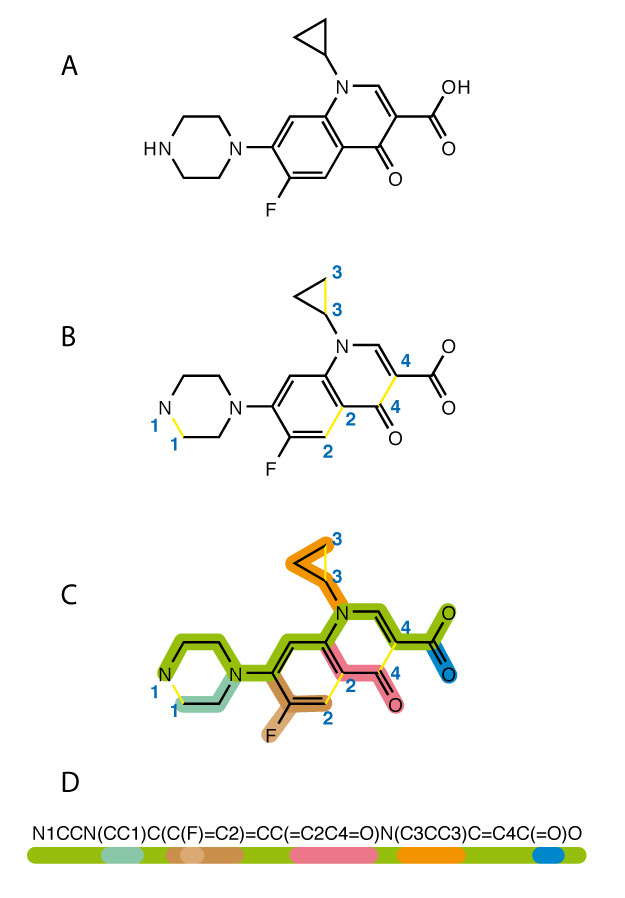
Each colour corresponds to a sequence of characters in a SMILES string
本文目標是使用遞歸神經網絡(RNN)生成新的分子。 De novo僅僅意味著從更簡單的分子合成新的複雜分子。 然而,有一個主要的警告:我們不知道這些分子有多麼有用,甚至它們的正確性,但在本文的最後會提到我們可以擴展這個模型的方法來做到這一點。 我們的想法是訓練模型學習SMILES字串中的模式,以便生成的輸出可以匹配有效的分子。 SMILES只是根據結構和不同組成的分子表示成字串(String),並且有助於讓電腦理解分子表示式。
參考
https://chemistry.stackexchange.com/questions/43299/is-there-a-way-to-use-free-software-to-convert-smiles-strings-to-structures/57358
此外,有個網站也可以將化學結構翻譯成SMILES字串:
https://cactus.nci.nih.gov/
由於我們將文本作為數據提供到RNN神經網絡,因此RNN是用於生成新SMILES字符串的最佳網絡。 大多數論文和研究人員建議使用LSTM增強RNN的內部結構,LSTM是一種更有效訓練文本的神經網路。 因此,我們將使用2 LSTM層,在100,000個SMILES字符串的數據集上進行訓練。
Stage 1 — Mapping
該項目的第一階段是創建一個將字元映射到整數,以便RNN可以處理數據,反之,也可以將結果和輸出轉換回字元時。 我們需要創建一組所有獨特字串,並enumerate(為每個字元定義一個數值)每個項目。 SMILES字串由兩種類型的字元組成,它們是特殊字元,如“/”或“=”,以及元素符號,如“P”,“Si”,“Mg”等。我們將這些enumerate的獨特字元放入一個 獨特的字典,
unique_chars = sorted(list(set(raw_text)))
char_to_int = dict((c, i) for i, c in enumerate(unique_chars))
char_to_int.update({-1 : "\n"})
這裡合併“\ n”表示為.txt文件中的新行。
Stage 2— Data Preprocessing
一旦我們為字元映射創建了字典,我們就會呼叫字典char_to_int將SMILES字串數據集中的每個字元轉換為整數。 Normalization是將字元的每個整數值除以數據集中獨特字元的數量。 然後,我們使用NumPy將輸入陣列X reshape為[樣本,時間步長,生理化學特徵]的三維陣列,這是循環模型的預期輸入格式。 輸出變量Y是one-hot encoding,以在訓練模型後生成新的SMILES。 One-hot encoding適用於整數表示,並且刪除整數編碼變量,並為每個獨特的整數值添加一個新的二進制(0或1)變量。
Stage 3— Model Architecture

The Model Architecture, consisting of two LSTM layers with 256 units (Gupta et al.)
這個系統結構的設計是根據Gupta等人的研究論文“De Novo Drug Design的Generative Recurrent Networks”。採用這種架構,因為它在創建有效的SMILES字串時產生了97%的準確率,而且它是一個非常簡單的架構。它由兩個LSTM層組成,每個層都有一個隱藏的狀態向量H,它透過一個單元傳遞先前的資訊給下一個單元,這是RNN以前從未見過的。像這樣的更多循環連接允許網絡理解SMILES序列的更複雜的依賴性。這些層上使用0.25的壓差正則化,接著是使用softmax激活函數的neutron組成密集輸出層。 Softmax是一個函數,它將K個實數的向量(在我們的例子中是輸出向量Y)作為輸入,並將其normalize為由K個概率組成的概率分佈。
# Create the model (simple 2 layer LSTM)
model = Sequential()
model.add(LSTM(128, input_shape=(X.shape[1], X.shape[2]), return_sequences = True))
model.add(Dropout(0.25))
model.add(LSTM(256, return_sequences = True))
model.add(Dropout(0.25))
model.add(LSTM(512, return_sequences = True))
model.add(Dropout(0.25))
model.add(LSTM(256, return_sequences = True))
model.add(Dropout(0.25))
model.add(LSTM(128))
model.add(Dropout(0.25))
model.add(Dense(Y.shape[1], activation='softmax'))
隨意添加更多層或更改dropout rate,但請記住,在NN(神經網絡)中有更多層和神經元,在計算上它獲得的強度和準確度越高。
Stage 4— Training:
這裡的神經網絡使用categorical cross entropy作為loss function,以及Adam Optimizer。 包含100,000個SMILES字串的數據集=訓練了10個epochs的模型以及512 batch_size來學習。 這裡的經驗法則是更多的epochs +更小的batch_size =更好地理解數據,但代價是需要更長的訓練時間。 我們還可以利用檢查點(checkpoints),它是Keras函式庫中的內建功能來保存我們的訓練進度,以及每個epoch的模型權重,以便稍後傳輸或保存。
Stage 5 — Generating New Molecules:
生成新分子相當簡單。 首先,我們加載預先訓練的權重,這樣我們就可以避免每次在生成新的SMILES字串之前訓練模型。 然後,我們從數據集中隨機選擇一個SMILES字串作為參考字串,並在範圍內生成指定數量的字元,並將整數值轉換回字元。 上面的代碼在技術上可以用於生成任何類型的文本,無論是故事,音樂還是SMILES分子。 根據自定義調整,學習速率,數據集大小和quality,結果會有所不同,但最後我們應該得到一種有效的分子表示字串。 在進行學習新的子結構和分支(N1CCN(CC1)C(C(F)=C2…)分子之前,模型可以藉由僅生成一個字符(NNNNNN)的序列開始。
這是分子二維結構 (O1C=C[C@H([C@H]1O2)c3c2cc(OC)c4c3OC(=O)C5=C4CCC(=O)5)

和三維結構:
O1C=C[C@H]([C@H]1O2)c3c2cc(OC)c4c3OC(=O)C5=C4CCC(=O)5
Possible Improvements
1. Checking the Validity of these Molecules:
我們不知道我們生成的分子是否具有任何用例, 我們必須藉由用於訓練的原始分子進行比較來驗證這些生成的分子是否是有效的分子結構。 藉由計算數據的共同生理化學特徵,以及對訓練數據的特徵使用主成分分析(Principal Component Analysis),我們可以確定新生成的分子是否相應地進行了轉換。
2. Are SMILES Strings even the most optimal way to represent molecules?:
如何確信LSTMs可以在最好的情況下生成文本的樣本,因為SMILES字串只是查看分子化學組成的基本方法。 我們可能會創建更好的方法來表示分子的複雜性,以便將來進行更準確的測試。 然而,目前,SMILES Strings和RNN是使用機器學習產生分子的規範。
3. The Dataset: Through data augmentation
我們可以採用不同SMILES字串的排列,並將它們添加到我們的數據集中。 增加數據集的另一種方法是enumerate SMILES字符串超出其原始形式,或以其他方式編寫。

Changing Drug Discovery: Fragment-Based Drug Discovery (FBDD)

這種產生分子的方法的主要用途之一是基於片段的藥物發現或FBDD。 這是在不使用哨兵(使用其存在作為終止條件的特殊值或特徵)開始輸入的地方,我們可以從已知結合目標疾病機制的片段開始。 通過將這個片段的SMILES字串作為輸入,我們可以用RNN逐漸“生長”分子的其餘部分,從而產生更有效地抵消某種功能的分子! 這種方法肯定有很多希望,並且看起來將來會被更多地使用會很有趣。
Conclusion + Key Takeaways
RNN僅使用數據集上的少量參數來提供了一種簡單而有效的分子生成方法。 該領域的大多數研究都希望結合RL或對抗性訓練等結構,以幫助增加產生的有效分子的數量,或使模型偏向於創造具有特定藥物某些特性的分子。 希望在未來採用這種方法,基於片段的藥物發現變得更加普遍,並有助於使藥物開發更加可行和經濟。 AI是移除創造療法的猜測的關鍵。
Key Takeaways
1. 緩慢而昂貴的藥物開發和材料科學研究是目前方法進展緩慢的直接結果
2. 使用機器學習,我們可以提高研發的速度。
3. 機器學習用於生成分子的最有效用途是使用RNN和SMILES分子字符串表示,但它們不是最佳方式。
4. 我們還有很長的路要走,才能使用人工智能以更快的速度製作更準確有效的分子結構,但還有很多值得期待的東西!
https://towardsdatascience.com/generating-molecules-with-the-help-of-recurrent-neural-networks-c3fe23bd0de2
但是,我們如何嘗試加速我們識別某些目標效應的化合物的方式? 在這種情況下,這就是生成網絡領域迅速普及,以幫助使用諸如RNN之類的網絡生成新分子的地方。 目標是通過去除盡可能多的過程來加速發現階段的過程,我們必須通過重新藥物設計(de novo drug design)手動測試大量化合物來識別有效的化合物。
Project De Novo: Generating Novel Molecules

Each colour corresponds to a sequence of characters in a SMILES string
本文目標是使用遞歸神經網絡(RNN)生成新的分子。 De novo僅僅意味著從更簡單的分子合成新的複雜分子。 然而,有一個主要的警告:我們不知道這些分子有多麼有用,甚至它們的正確性,但在本文的最後會提到我們可以擴展這個模型的方法來做到這一點。 我們的想法是訓練模型學習SMILES字串中的模式,以便生成的輸出可以匹配有效的分子。 SMILES只是根據結構和不同組成的分子表示成字串(String),並且有助於讓電腦理解分子表示式。
from rdkit import Chem
from rdkit.Chem import Draw
import matplotlib.pyplot as plt
%matplotlib inline
penicillin_g_smiles = 'CC1([C@@H](N2[C@H](S1)[C@@H](C2=O)NC(=O)Cc3ccccc3)C(=O)O)C'
penicillin_g = Chem.MolFromSmiles(penicillin_g_smiles)
Draw.MolToMPL(penicillin_g, size=(200, 200))參考
https://chemistry.stackexchange.com/questions/43299/is-there-a-way-to-use-free-software-to-convert-smiles-strings-to-structures/57358
此外,有個網站也可以將化學結構翻譯成SMILES字串:
https://cactus.nci.nih.gov/
由於我們將文本作為數據提供到RNN神經網絡,因此RNN是用於生成新SMILES字符串的最佳網絡。 大多數論文和研究人員建議使用LSTM增強RNN的內部結構,LSTM是一種更有效訓練文本的神經網路。 因此,我們將使用2 LSTM層,在100,000個SMILES字符串的數據集上進行訓練。
Stage 1 — Mapping
該項目的第一階段是創建一個將字元映射到整數,以便RNN可以處理數據,反之,也可以將結果和輸出轉換回字元時。 我們需要創建一組所有獨特字串,並enumerate(為每個字元定義一個數值)每個項目。 SMILES字串由兩種類型的字元組成,它們是特殊字元,如“/”或“=”,以及元素符號,如“P”,“Si”,“Mg”等。我們將這些enumerate的獨特字元放入一個 獨特的字典,
unique_chars = sorted(list(set(raw_text)))
char_to_int = dict((c, i) for i, c in enumerate(unique_chars))
char_to_int.update({-1 : "\n"})
這裡合併“\ n”表示為.txt文件中的新行。
Stage 2— Data Preprocessing
一旦我們為字元映射創建了字典,我們就會呼叫字典char_to_int將SMILES字串數據集中的每個字元轉換為整數。 Normalization是將字元的每個整數值除以數據集中獨特字元的數量。 然後,我們使用NumPy將輸入陣列X reshape為[樣本,時間步長,生理化學特徵]的三維陣列,這是循環模型的預期輸入格式。 輸出變量Y是one-hot encoding,以在訓練模型後生成新的SMILES。 One-hot encoding適用於整數表示,並且刪除整數編碼變量,並為每個獨特的整數值添加一個新的二進制(0或1)變量。
Stage 3— Model Architecture

The Model Architecture, consisting of two LSTM layers with 256 units (Gupta et al.)
這個系統結構的設計是根據Gupta等人的研究論文“De Novo Drug Design的Generative Recurrent Networks”。採用這種架構,因為它在創建有效的SMILES字串時產生了97%的準確率,而且它是一個非常簡單的架構。它由兩個LSTM層組成,每個層都有一個隱藏的狀態向量H,它透過一個單元傳遞先前的資訊給下一個單元,這是RNN以前從未見過的。像這樣的更多循環連接允許網絡理解SMILES序列的更複雜的依賴性。這些層上使用0.25的壓差正則化,接著是使用softmax激活函數的neutron組成密集輸出層。 Softmax是一個函數,它將K個實數的向量(在我們的例子中是輸出向量Y)作為輸入,並將其normalize為由K個概率組成的概率分佈。
# Create the model (simple 2 layer LSTM)
model = Sequential()
model.add(LSTM(128, input_shape=(X.shape[1], X.shape[2]), return_sequences = True))
model.add(Dropout(0.25))
model.add(LSTM(256, return_sequences = True))
model.add(Dropout(0.25))
model.add(LSTM(512, return_sequences = True))
model.add(Dropout(0.25))
model.add(LSTM(256, return_sequences = True))
model.add(Dropout(0.25))
model.add(LSTM(128))
model.add(Dropout(0.25))
model.add(Dense(Y.shape[1], activation='softmax'))
隨意添加更多層或更改dropout rate,但請記住,在NN(神經網絡)中有更多層和神經元,在計算上它獲得的強度和準確度越高。
Stage 4— Training:
這裡的神經網絡使用categorical cross entropy作為loss function,以及Adam Optimizer。 包含100,000個SMILES字串的數據集=訓練了10個epochs的模型以及512 batch_size來學習。 這裡的經驗法則是更多的epochs +更小的batch_size =更好地理解數據,但代價是需要更長的訓練時間。 我們還可以利用檢查點(checkpoints),它是Keras函式庫中的內建功能來保存我們的訓練進度,以及每個epoch的模型權重,以便稍後傳輸或保存。
# Define checkpoints (used to save the weights at each epoch, so that the model doesn't need to be retrained) filepath="weights-improvement-{epoch:02d}-{loss:.4f}.hdf5"checkpoint = ModelCheckpoint(filepath, monitor = 'loss', verbose = 1, save_best_only = True, mode = 'min') callbacks_list = [checkpoint] # Fit the model model.fit(X, Y, epochs = 19, batch_size = 512, callbacks = callbacks_list) """TO TRAIN FROM SAVED CHECKPOINT""" # Load weights model.load_weights("weights-improvement-75-1.8144.hdf5") # load the model new_model = load_model ("model.h5") assert_allclose(model.predict(x_train),new_model.predict(x_train), 1e-5) # fit the model checkpoint = ModelCheckpoint(filepath, monitor='loss', verbose=1, save_best_only=True, mode='min') callbacks_list = [checkpoint]new_model.fit(x_train, y_train, epochs = 100, batch_size = 64, callbacks = callbacks_list)
Stage 5 — Generating New Molecules:
生成新分子相當簡單。 首先,我們加載預先訓練的權重,這樣我們就可以避免每次在生成新的SMILES字串之前訓練模型。 然後,我們從數據集中隨機選擇一個SMILES字串作為參考字串,並在範圍內生成指定數量的字元,並將整數值轉換回字元。 上面的代碼在技術上可以用於生成任何類型的文本,無論是故事,音樂還是SMILES分子。 根據自定義調整,學習速率,數據集大小和quality,結果會有所不同,但最後我們應該得到一種有效的分子表示字串。 在進行學習新的子結構和分支(N1CCN(CC1)C(C(F)=C2…)分子之前,模型可以藉由僅生成一個字符(NNNNNN)的序列開始。
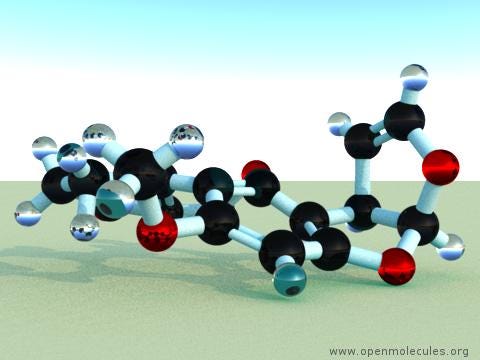
這是分子二維結構 (O1C=C[C@H([C@H]1O2)c3c2cc(OC)c4c3OC(=O)C5=C4CCC(=O)5)

和三維結構:
O1C=C[C@H]([C@H]1O2)c3c2cc(OC)c4c3OC(=O)C5=C4CCC(=O)5

Possible Improvements
1. Checking the Validity of these Molecules:
我們不知道我們生成的分子是否具有任何用例, 我們必須藉由用於訓練的原始分子進行比較來驗證這些生成的分子是否是有效的分子結構。 藉由計算數據的共同生理化學特徵,以及對訓練數據的特徵使用主成分分析(Principal Component Analysis),我們可以確定新生成的分子是否相應地進行了轉換。
2. Are SMILES Strings even the most optimal way to represent molecules?:
如何確信LSTMs可以在最好的情況下生成文本的樣本,因為SMILES字串只是查看分子化學組成的基本方法。 我們可能會創建更好的方法來表示分子的複雜性,以便將來進行更準確的測試。 然而,目前,SMILES Strings和RNN是使用機器學習產生分子的規範。
3. The Dataset: Through data augmentation
我們可以採用不同SMILES字串的排列,並將它們添加到我們的數據集中。 增加數據集的另一種方法是enumerate SMILES字符串超出其原始形式,或以其他方式編寫。

Changing Drug Discovery: Fragment-Based Drug Discovery (FBDD)

這種產生分子的方法的主要用途之一是基於片段的藥物發現或FBDD。 這是在不使用哨兵(使用其存在作為終止條件的特殊值或特徵)開始輸入的地方,我們可以從已知結合目標疾病機制的片段開始。 通過將這個片段的SMILES字串作為輸入,我們可以用RNN逐漸“生長”分子的其餘部分,從而產生更有效地抵消某種功能的分子! 這種方法肯定有很多希望,並且看起來將來會被更多地使用會很有趣。
Conclusion + Key Takeaways
RNN僅使用數據集上的少量參數來提供了一種簡單而有效的分子生成方法。 該領域的大多數研究都希望結合RL或對抗性訓練等結構,以幫助增加產生的有效分子的數量,或使模型偏向於創造具有特定藥物某些特性的分子。 希望在未來採用這種方法,基於片段的藥物發現變得更加普遍,並有助於使藥物開發更加可行和經濟。 AI是移除創造療法的猜測的關鍵。
Key Takeaways
1. 緩慢而昂貴的藥物開發和材料科學研究是目前方法進展緩慢的直接結果
2. 使用機器學習,我們可以提高研發的速度。
3. 機器學習用於生成分子的最有效用途是使用RNN和SMILES分子字符串表示,但它們不是最佳方式。
4. 我們還有很長的路要走,才能使用人工智能以更快的速度製作更準確有效的分子結構,但還有很多值得期待的東西!
https://towardsdatascience.com/generating-molecules-with-the-help-of-recurrent-neural-networks-c3fe23bd0de2
2019年9月15日 星期日
2019年9月14日 星期六
2019年9月11日 星期三
2019年9月10日 星期二
A reactive force field implementation in LAMMPS
LAMMPS在reax範例中的input腳本(in.CHO)
https://github.com/lammps/lammps/blob/master/examples/reax/CHO/in.CHO
其中data檔(data.CHO)為
https://github.com/lammps/lammps/blob/master/examples/reax/CHO/data.CHO
reax的建模需要注意的是units選取real,atom_style為charge
讀取模型的數據文件,可以嘗試用MS輸出car格式,利用LAMMPS中的msi2lmp工具轉化為所需的數據文件
接著選取potential類型,注意pair_style和pair_coeff應在read_data或create_box後
上述命令中lmp_control為控製文件,用於控制輸出軌跡文件trj,若無需要可將其替換為NULL
ffield.reax.cho存放在Lammps的potential資料夾
https://github.com/lammps/lammps/tree/master/potentials
,在使用其他系統時,可以選用ADF軟件中的potential文件(可以直接使用)。
對於reax的分子動力學模擬,必須有電荷守恆條件(fix qeq / reax),其中param.qeq存放所需原子的參數,從左到右分別為原子類型,電負性(eV),自庫倫勢,軌道指數
上述數值也存在於potential文件中,因此可以將param.qeq替換為REAX/ C,如下圖所示:
其次在進行模擬時,一般可以選用NVT,如果系統分子個數比較少,應增大溫度加快反應進程(去掉fix 1和fix 3改為)
reax的分子動力學模擬,time step應在0.1-1.0之間,一般選取0.25
執行後若要製作動畫,應生成dump文件
畫圖檔指令
topo readlammpsdata data.CHO charge
https://github.com/lammps/lammps/blob/master/examples/reax/CHO/in.CHO
# REAX potential for CHO system
# .....
units real
atom_style charge
read_data data.CHO
pair_style reax/c lmp_control
pair_coeff * * ffield.reax.cho H C O
neighbor 2 bin
neigh_modify every 10 delay 0 check no
fix 1 all nve
fix 2 all qeq/reax 1 0.0 10.0 1e-6 param.qeq
fix 3 all temp/berendsen 500.0 500.0 100.0
timestep 0.25
#dump 1 all atom 30 dump.reax.cho
run 3000其中data檔(data.CHO)為
https://github.com/lammps/lammps/blob/master/examples/reax/CHO/data.CHO
# CHO example
105 atoms
3 atom types
0 25.000 xlo xhi
0 25.000 ylo yhi
0 25.000 zlo zhi
Masses
1 1.0080
2 12.0107
3 15.9994
Atoms
1 2 0.0 10.67229 14.36836 12.47166
2 1 0.0 11.02446 14.91550 13.35233
3 1 0.0 11.02446 14.91549 11.59096
4 1 0.0 9.57932 14.41980 12.47166
5 2 0.0 11.17534 12.87608 12.47165
6 1 0.0 10.79792 12.33546 13.34037
7 1 0.0 10.79790 12.33545 11.60294
8 2 0.0 12.75013 12.93134 12.47163
9 1 0.0 13.13241 13.47175 11.60486
10 1 0.0 13.13241 13.47210 13.33818
11 2 0.0 13.22294 11.42815 12.47199
12 1 0.0 12.83858 10.89166 11.60377
13 1 0.0 12.83959 10.89255 13.34119
14 2 0.0 14.79762 11.45137 12.47107
15 1 0.0 15.21044 10.43808 12.47354
16 1 0.0 15.19550 11.96345 11.58877
17 1 0.0 15.19648 11.96815 13.35018
18 2 0.0 0.24250 0.91354 1.10383
19 1 0.0 0.97225 1.67509 1.39797
20 1 0.0 24.87363 1.18825 0.11010
21 1 0.0 24.39847 0.98637 1.79630
22 2 0.0 0.86944 24.46895 1.11508
23 1 0.0 1.21047 24.19771 2.11484
24 1 0.0 0.12679 23.71752 0.84453
25 2 0.0 2.06454 24.48829 0.08825
26 1 0.0 1.72846 24.75977 24.08683
27 1 0.0 2.80951 0.23920 0.35408
28 2 0.0 2.67036 23.03401 0.12171
29 1 0.0 1.92204 22.28680 24.85503
30 1 0.0 3.00638 22.76782 1.12450
31 2 0.0 3.87027 23.02208 24.10132
32 1 0.0 4.35176 22.04072 24.06515
33 1 0.0 3.54082 23.26189 23.08511
34 1 0.0 4.63935 23.75310 24.37121
35 2 0.0 1.37929 14.62909 17.52744
36 1 0.0 1.08393 15.52196 18.08818
37 1 0.0 2.47385 14.59977 17.52258
38 1 0.0 1.05260 14.77122 16.49293
39 2 0.0 0.76275 13.31937 18.14786
40 1 0.0 24.67295 13.35030 18.12450
41 1 0.0 1.04396 12.44064 17.56651
42 2 0.0 1.30113 13.22425 19.62581
43 1 0.0 2.39107 13.19385 19.65447
44 1 0.0 1.02336 14.10169 20.21106
45 2 0.0 0.66878 11.90830 20.21883
46 1 0.0 0.94960 11.03396 19.63080
47 1 0.0 24.57945 11.94426 20.18968
48 2 0.0 1.19125 11.78568 21.69954
49 1 0.0 0.79365 10.89123 22.18875
50 1 0.0 2.28374 11.72162 21.74071
51 1 0.0 0.89616 12.64769 22.30679
52 2 0.0 11.41750 7.16471 22.76002
53 1 0.0 11.74866 7.28340 21.72336
54 1 0.0 11.72154 8.06612 23.30055
55 1 0.0 11.97469 6.32478 23.18558
56 2 0.0 9.86319 6.92474 22.85179
57 1 0.0 9.57626 6.01094 22.33031
58 1 0.0 9.54930 6.78307 23.88660
59 2 0.0 9.17390 8.18942 22.21244
60 1 0.0 9.45849 9.10599 22.73021
61 1 0.0 9.48557 8.33580 21.17777
62 2 0.0 7.62459 7.92132 22.31840
63 1 0.0 7.31756 7.77569 23.35472
64 1 0.0 7.34468 7.00469 21.79795
65 2 0.0 6.90692 9.17258 21.68631
66 1 0.0 5.81845 9.06496 21.71809
67 1 0.0 7.15914 10.09632 22.21721
68 1 0.0 7.18992 9.31630 20.63835
69 2 0.0 4.69047 14.13340 23.48572
70 1 0.0 4.95366 15.17281 23.26391
71 1 0.0 5.39163 13.78010 24.24888
72 1 0.0 4.87514 13.55000 22.57874
73 2 0.0 3.19477 13.99798 23.95930
74 1 0.0 2.50599 14.33002 23.18163
75 1 0.0 2.93803 12.95591 24.15345
76 2 0.0 3.05322 14.87431 0.26136
77 1 0.0 3.74058 14.54651 1.04202
78 1 0.0 3.30993 15.91730 0.07257
79 2 0.0 1.55058 14.71961 0.71013
80 1 0.0 1.29864 13.67531 0.89801
81 1 0.0 0.86725 15.05003 24.92701
82 2 0.0 1.37850 15.58633 2.01380
83 1 0.0 0.35341 15.53527 2.39297
84 1 0.0 2.04062 15.24695 2.81709
85 1 0.0 1.60704 16.64178 1.83261
86 3 0.0 8.51658 13.05007 22.43728
87 3 0.0 9.43965 13.72051 21.88842
88 3 0.0 18.16518 4.73455 8.81928
89 3 0.0 18.65469 4.57291 7.66370
90 3 0.0 6.43553 20.34119 24.80049
91 3 0.0 6.44898 20.31621 23.53493
92 3 0.0 21.90539 11.54301 19.82384
93 3 0.0 20.76137 11.61918 20.36007
94 3 0.0 3.42232 11.07545 5.77130
95 3 0.0 3.88671 10.95299 4.60048
96 3 0.0 11.93988 4.94134 20.86058
97 3 0.0 12.98804 5.47798 20.39555
98 3 0.0 14.08646 9.50799 20.80806
99 3 0.0 14.09449 10.68237 20.33642
100 3 0.0 3.45246 19.93144 16.38965
101 3 0.0 2.86282 19.60263 15.31936
102 3 0.0 12.85008 21.95287 13.63796
103 3 0.0 12.06593 21.16486 14.24238
104 3 0.0 24.47055 7.42219 14.24997
105 3 0.0 24.43181 7.37102 12.98624reax的建模需要注意的是units選取real,atom_style為charge
units real
atom_style charge讀取模型的數據文件,可以嘗試用MS輸出car格式,利用LAMMPS中的msi2lmp工具轉化為所需的數據文件
read_data data.CHO接著選取potential類型,注意pair_style和pair_coeff應在read_data或create_box後
pair_style reax/c lmp_control
pair_coeff * * ffield.reax.cho H C O
neighbor 2 bin
neigh_modify every 10 delay 0 check no上述命令中lmp_control為控製文件,用於控制輸出軌跡文件trj,若無需要可將其替換為NULL
ffield.reax.cho存放在Lammps的potential資料夾
https://github.com/lammps/lammps/tree/master/potentials
,在使用其他系統時,可以選用ADF軟件中的potential文件(可以直接使用)。
fix 1 all nve
fix 2 all qeq/reax 1 0.0 10.0 1e-6 param.qeq
fix 3 all temp/berendsen 500.0 500.0 100.0對於reax的分子動力學模擬,必須有電荷守恆條件(fix qeq / reax),其中param.qeq存放所需原子的參數,從左到右分別為原子類型,電負性(eV),自庫倫勢,軌道指數
1 5.3200 14.8732 1.0206
2 5.8678 14.0000 0.9000
3 8.5000 17.9978 1.0503上述數值也存在於potential文件中,因此可以將param.qeq替換為REAX/ C,如下圖所示:
其次在進行模擬時,一般可以選用NVT,如果系統分子個數比較少,應增大溫度加快反應進程(去掉fix 1和fix 3改為)
fix 1 all nvt temp 3500.0 3500.0 100.0
timestep 0.25執行後若要製作動畫,應生成dump文件
dump 1 all custom mass type xs ys zs fx fy fz畫圖檔指令
topo readlammpsdata data.CHO charge
2019年9月9日 星期一
2019年9月7日 星期六
2019年9月6日 星期五
2019年9月4日 星期三
Windows安裝tensorflow和Keras讓jupyter notebook可以執行
打開Anaconda Prompt,因為安裝anaconda時沒有指定環境變數,所以只能在Anaconda Prompt終端機呼叫conda
$ conda create -n tensorflow python=3.6
$ activate tensorflow
$ pip install tensorflow
$ pip install keras
$ pip install jupyter
$ jupyter notebook
2019年9月3日 星期二
訂閱:
文章 (Atom)





